Publikationen 2024
OTULIN-related conditions: Report of a new case and review of the literature using GenIA. Caballero-Oteyza A, Crisponi L, Peng XP, Wang H, Mrovecova P, Olla S, Siguri C, Marnissi F, Jouhadi Z, Aksentijevich I, Grimbacher B, Proietti Clin Immunol. 2024 Jun 22;265:110292. Epub ahead of print.
37 Oral microbiome’s impact on mucositis and locoregional tumor control in HNSCC patients undergoing radiotherapy. A Rühle, EBM Ordonez, M Krausz, AR Thomsen, D Schnell, T Sprave, …Radiotherapy and Oncology 192, S75-S77
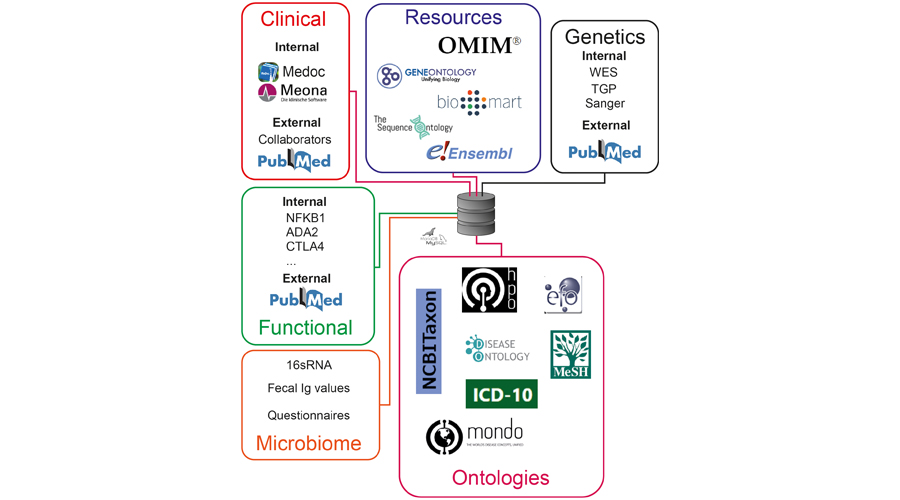
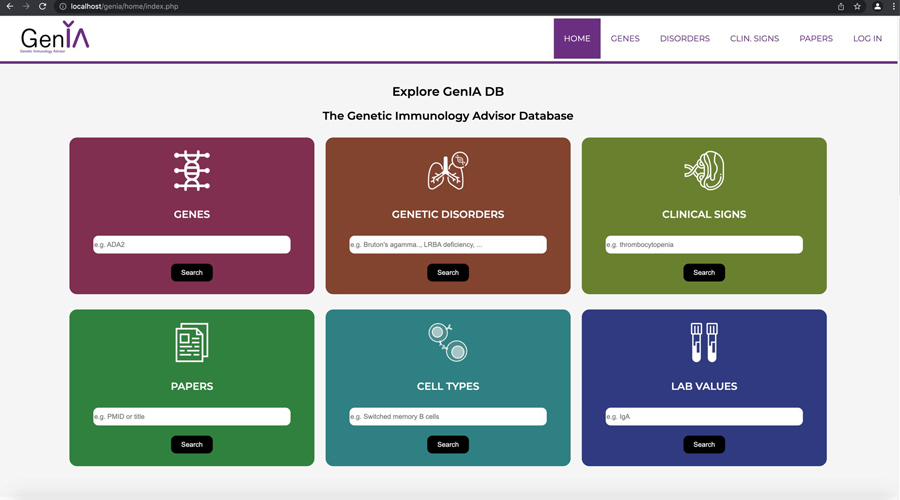
GenIA, the Genetic Immunology Advisor database for inborn errors of immunity A Caballero-Oteyza, L Crisponi, XP Peng, K Yauy, S Volpi, S Giardino, …Journal of Allergy and Clinical Immunology 153 (3), 831-843
Diagnostic evaluation of paediatric autoimmune lymphoproliferative immunodeficiencies (ALPID): a prospective cohort study. Hägele P, Staus P, Scheible R, Uhlmann A, Heeg M, Klemann C, Maccari ME, Ritterbusch H, Armstrong M, Cutcutache I, Elliott KS, von Bernuth H, Leahy TR, Leyh J, Holzinger D, Lehmberg K, Svec P, Masjosthusmann K, Hambleton S, Jakob M, Sparber-Sauer M, Kager L, Puzik A, Wolkewitz M, Lorenz MR, Schwarz K, Speckmann C, Rensing-Ehl A, Ehl S; ALPID study group. Lancet Haematol. 2024 Feb;11(2):e114-e126. Erratum in: Lancet Haematol. 2024 Apr;11(4):e248.
A 14-Day Double-Blind, Randomized, Controlled Crossover Intervention Study with Anti-Bacterial Benzyl Isothiocyanate from Nasturtium (Tropaeolum majus) on Human Gut Microbiome and Host Defense. Pfäffle SP, Herz C, Brombacher E, Proietti M, Gigl M, Hofstetter CK, Mittermeier-Kleßinger VK, Claßen S, Tran HTT, Dawid C, Kreutz C, Günther S, Lamy E. Nutrients. 2024 Jan 26;16(3):373.
Lipocalin-2 expression identifies an intestinal regulatory neutrophil population during acute graft-versus-host disease. Czech M, Schneider S, Peltokangas N, El Khawanky N, Ghimire S, Andrieux G, Hülsdünker J, Krausz M, Proietti M, Braun LM, Rückert T, Langenbach M, Schmidt D, Martin I, Wenger V, de Vega E, Haring E, Pourjam M, Pfeifer D, Schmitt-Graeff A, Grimbacher B, Aumann K, Kircher B, Tilg H, Raffatellu M, Thiele Orberg E, Häcker G, Duyster J, Köhler N, Holler E, Nachbaur D, Boerries M, Gerner RR, Grün D, Zeiser R. Sci Transl Med. 2024 Feb 21;16(735):eadi1501. Epub 2024 Feb 21.
A Novel Transmembrane CXCR4 Variant That Expands the WHIM Genotype-Phenotype Paradigm. Zmajkovicova K, Pawar S, Sharapova SO, Geier CB, Wiest I, Nguyen C, Monticelli H, Maier-Munsa S, Chen K, Sleasman JW, Aleshkevich S, Polyakova E, Sakovich I, Warnatz K, Grimbacher B, Proietti M, Sondheimer N, Ujhazi B, Gordon S, Ellison M, Yilmaz M, Walter JE, Badarau A, Taveras AG, Neff JL, Bledsoe JR, Tarrant TK. Blood Adv. 2024 May 20:bloodadvances.2023011875. Epub ahead of print.
ADA2 is a lysosomal deoxyadenosine deaminase acting on DNA involved in regulating TLR9-mediated immune sensing of DNAO. K. Greiner-Tollersrud, M. Krausz, V. Boehler, A. Polyzou, M. Seidl, A. Spahiu, et al.
Publikationen 2023
Clinical, immunological and molecular findings of 8 patients with typical and atypical severe combined immunodeficiency: identification of 7 novel mutations by whole exome sequencing. Alizadeh Z, Fazlollahi MR, Mazinani M, Badalzadeh M, Heydarlou H, Carapito R, Molitor A, de Oteyza ACG, Proietti M, Bavani MS, Shariat M, Fallahpour M, Movahedi M, Moradi L, Grimbacher B, Bahram S, Pourpak Z. Genes Immun. 2023 Aug;24(4):207-214. Epub 2023 Jul 29.
Fecal Immunoglobulin Levels as a Modifier of the Gut Microbiome in Patients with Common Variable Immunodeficiency. J Clin Immunol. Nöltner C, Bulashevska A, Hübscher K, Haberstroh H, Grimbacher B, Proietti M. 2023 Aug;43(6):1208-1220. Epub 2023 Mar 24.
ARPC5 deficiency leads to severe early-onset systemic inflammation and mortality. Sindram E, Caballero-Oteyza A, Kogata N, Chor Mei Huang S, Alizadeh Z, Gámez-Díaz L, Fazlollhi MR, Peng X, Grimbacher B, Way M, Proietti M. Dis Model Mech. 2023 Jul 1;16(7):dmm050145. Epub 2023 Jul 20.
Interferon-Driven Immune Dysregulation in Common Variable Immunodeficiency-Associated Villous Atrophy and Norovirus Infection. Strohmeier V, Andrieux G, Unger S, Pascual-Reguant A, Klocperk A, Seidl M, Marques OC, Eckert M, Gräwe K, Shabani M, von Spee-Mayer C, Friedmann D, Harder I, Gutenberger S, Keller B, Proietti M, Bulashevska A, Grimbacher B, Provaznik J, Benes V, Goldacker S, Schell C, Hauser AE, Boerries M, Hasselblatt P, Warnatz K. J Clin Immunol. 2023 Feb;43(2):371-390. Epub 2022 Oct 25.
Telomere biology disorders may manifest as common variable immunodeficiency (CVID). Rolles B, Caballero-Oteyza A, Proietti M, Goldacker S, Warnatz K, Camacho-Ordonez N, Prader S, Schmid JP, Vieri M, Isfort S, Meyer R, Kirschner M, Brümmendorf TH, Beier F, Grimbacher B. Clin Immunol. 2023 Dec;257:109837. Epub 2023 Nov 8.
Makrozytäre Anämie und Polychondritis: VEXAS-Syndrom [Macrocytic anemia and polychondritis: VEXAS syndrome]. Zeisbrich M, Schindler V, Krausz M, Proietti M, Mrovecova P, Voll RE, Glaser C, Röther F, Warnatz K, Venhoff N. Z Rheumatol. 2024 Apr;83(3):229-233. German. Epub 2023 Feb 3.
CVID-Associated B Cell Activating Factor Receptor Variants Change Receptor Oligomerization, Ligand Binding, and Signaling Responses. Block V, Sevdali E, Recher M, Abolhassani H, Hammarstrom L, Smulski CR, Baronio M, Plebani A, Proietti M, Speletas M, Warnatz K, Voll RE, Lougaris V, Schneider P, Eibel H. J Clin Immunol. 2023 Feb;43(2): 391-405. Epub 2022 Oct 29.
Publikationen 2022
Copy Number Analysis in a Large Cohort Suggestive of Inborn Errors of Immunity Indicates a Wide Spectrum of Relevant Chromosomal Losses and Gains. Wan R, Schieck M, Caballero-Oteyza A, Hofmann W, Cochino AV, Shcherbina A, Sherkat R, Wache-Mainier C, Fernandez A, Sultan M, Illig T, Grimbacher B, Proietti M, Steinemann D. J Clin Immunol. 2022 Jul;42(5):1083-1092. Epub 2022 Apr 29.
Clinical, Immunological and Molecular Findings of Patients with Severe Combined Immunodeficiency: Introducing of 7 Novel Mutations in 7 Genes. Z Alizadeh, MR Fazlollahi, M Mazinani, M Badalzadeh, H Heydarlou, …
Interferon-Driven Immune Dysregulation in Common Variable Immunodeficiency-Associated Villous Atrophy and Norovirus Infection. Strohmeier V, Andrieux G, Unger S, Pascual-Reguant A, Klocperk A, Seidl M, Marques OC, Eckert M, Gräwe K, Shabani M, von Spee-Mayer C, Friedmann D, Harder I, Gutenberger S, Keller B, Proietti M, Bulashevska A, Grimbacher B, Provaznik J, Benes V, Goldacker S, Schell C, Hauser AE, Boerries M, Hasselblatt P, Warnatz K. J Clin Immunol. 2023 Feb;43(2):371-390. Epub 2022 Oct 25.
Multi-omics analysis of naïve B cells of patients harboring the C104R mutation in TACI. Ramirez N, Posadas-Cantera S, Langer N, de Oteyza ACG, Proietti M, Keller B, Zhao F, Gernedl V, Pecoraro M, Eibel H, Warnatz K, Ballestar E, Geiger R, Bossen C, Grimbacher B. Front Immunol. 2022 Aug 16;13:938240.
Evaluation of Laboratory and Sonographic Parameters for Detection of Portal Hypertension in Patients with Common Variable Immunodeficiency. Globig AM, Strohmeier V, Surabattula R, Leeming DJ, Karsdal MA, Heeg M, Kindle G, Goldacker S, von Spee-Mayer C, Proietti M, Bausch B, Bettinger D, Schultheiß M, Thimme R, Schuppan D, Warnatz K. J Clin Immunol. 2022 Nov;42(8):1626-1637. Epub 2022 Jul 11.
Therapeutic targeting of endoplasmic reticulum stress in acute graft-versus-host disease. Haring E, Andrieux G, Uhl FM, Krausz M, Proietti M, Sauer B, Esser PR, Martin SF, Pfeifer D, Schmitt-Graeff A, Duyster J, Köhler N, Grimbacher B, Boerries M, Aumann K, Zeiser R, Apostolova P. Haematologica. 2022 Jul 1;107(7):1538-1554.
Publikationen 2021
Multiple Immunostainings with Different Epitope Retrievals-The FOLGAS Protocol. von Schoenfeld A, Bronsert P, Poc M, Fuller A, Filby A, Kraft S, Kurowski K, Sörensen K, Huber J, Pfeiffer J, Proietti M, Stehl V, Werner M, Seidl M. Int J Mol Sci. 2021 Dec 25;23(1):223.
Establishing the Molecular Diagnoses in a Cohort of 291 Patients With Predominantly Antibody Deficiency by Targeted Next-Generation Sequencing: Experience From a Monocentric Study. Rojas-Restrepo J, Caballero-Oteyza A, Huebscher K, Haberstroh H, Fliegauf M, Keller B, Kobbe R, Warnatz K, Ehl S, Proietti M *, Grimbacher B *. Front Immunol. 2021 Dec 17;12:786516.
Genetic Analysis of a Cohort of 275 Patients with Hyper-IgE Syndromes and/or Chronic Mucocutaneous Candidiasis. Frede N, Rojas-Restrepo J, Caballero Garcia de Oteyza A, Buchta M, Hübscher K, Gámez-Díaz L, Proietti M, Saghafi S, Chavoshzadeh Z, Soler-Palacin P, Galal N, Adeli M, Aldave-Becerra JC, Al-Ddafari MS, Ardenyz Ö, Atkinson TP, Kut FB, Çelmeli F, Rees H, Kilic SS, Kirovski I, Klein C, Kobbe R, Korganow AS, Lilic D, Lunt P, Makwana N, Metin A, Özgür TT, Karakas AA, Seneviratne S, Sherkat R, Sousa AB, Unal E, Patiroglu T, Wahn V, von Bernuth H, Whiteford M, Doffinger R, Jouhadi Z, Grimbacher B. J Clin Immunol. 2021 Nov;41(8):1804-1838.
Altered Spectrum of Lymphoid Neoplasms in a Single-Center Cohort of Common Variable Immunodeficiency with Immune Dysregulation. Wehr C, Houet L, Unger S, Kindle G, Goldacker S, Grimbacher B, Caballero Garcia de Oteyza A, Marks R, Pfeifer D, Nieters A, Proietti M, Warnatz K, Schmitt-Graeff A. J Clin Immunol. 2021 Aug;41(6):1250-1265. Epub 2021 Apr 19.
Gain-of-function variants in SYK cause immune dysregulation and systemic inflammation in humans and mice. Wang L, Aschenbrenner D, Zeng Z, Cao X, Mayr D, Mehta M, Capitani M, Warner N, Pan J, Wang L, Li Q, Zuo T, Cohen-Kedar S, Lu J, Ardy RC, Mulder DJ,
Dissanayake D, Peng K, Huang Z, Li X, Wang Y, Wang X, Li S, Bullers S, Gammage AN, Warnatz K, Schiefer AI, Krivan G, Goda V, Kahr WHA, Lemaire M; Genomics England Research Consortium, Lu CY, Siddiqui I, Surette MG, Kotlarz D, Engelhardt KR, Griffin HR, Rottapel R, Decaluwe H, Laxer RM, Proietti M,
Hambleton S, Elcombe S, Guo CH, Grimbacher B, Dotan I, Ng SC, Freeman SA, Snapper SB, Klein C, Boztug K, Huang Y, Li D, Uhlig HH, Muise AM. Nat Genet. 2021 Apr;53(4):500-510. Epub 2021 Mar 29. Erratum in: Nat Genet. 2022 Feb;54(2):213.
Agammaglobulinemia with normal B-cell numbers in a patient lacking Bob1. J Allergy Clin Immunol. 2021 May;147(5):1977-1980. Kury P, Staniek J, Wegehaupt O, Janowska I, Eckenweiler M, Korinthenberg R, Japaridze N, Pendziwiat M, Helbig I, Verhoeyen E, Jung J, Garcia de Oteyza AC, Proietti M, Phirtskhalaishvili T, Rtskhiladze I, Nielsen PJ, Ehl S, Speckmann C, Rizzi M. Epub 2021 Feb 9.
Bile acids regulate intestinal antigen presentation and reduce graft-versus-host disease without impairing the graft-versus-leukemia effect. Haring E, Uhl FM, Andrieux G, Proietti M, Bulashevska A, Sauer B, Braun LM, de Vega Gomez E, Esser PR, Martin SF, Pfeifer D, Follo M, Schmitt-Graeff A, Buescher J, Duyster J, Grimbacher B, Boerries M, Pearce EL, Zeiser R, Apostolova P. Haematologica. 2021 Aug 1;106(8):2131-2146.